维权声明:本文为jimzhu原创作品,本作者与仪器信息网是该作品合法使用者,该作品暂不对外授权转载。其他任何网站、组织、单位或个人等将该作品在本站以外的任何媒体任何形式出现均属侵权违法行为,我们将追究法律责任。
Amdis解卷积软件初步应用(12)----难分离共流峰处理实例1
先回顾一下AMDIS的基本概念
对于AMDIS有的网友可能比较熟悉,特别是农残,环境,有害物,香精香料等领域的朋友可能属于高级使用者。本人以初学者的身份初步介绍一下AMDIS。如有不妥,请批评指正。
一般来说,目标化合物的分析要求检测目标离子和确认离子的比例。然而,对于高基体
背景的样品,大峰后面的痕量组分或流出时间很接近的成分,离子比例会受到基体的影响很难符合要求。为了确保分析结果可靠,一般采用背景扣除及手动积分。因此,对于复杂基体的样品数据处理,需要耗费大量的时间。为了提高分析效率,谱图可以利用一种称为“解卷积”的数学计算来将目标化合物从背景中分离出来。美国国家标准和技术院(NIST)开发了功能强大的解卷积软件,即自动质谱解卷积和鉴定系统(AMDIS)。
下面简单介绍一下AMDIS:
AMDIS软件由美国国家标准技术研究院(NIST)(National Institute ofStandards and Technology)提供。
The
Automatic
Mass Spectral
Deconvolutionand
Identification
System (AMDIS)
自动质谱图解卷积和鉴定系统软件(AMDIS)让您从GC/MS数据文件自动找到目标化合物。软件先对GC/MS数据文件解卷积寻找所有分离组分。每一组分与目标化合物的谱库进行对比。如果以上的用户设定值,然后报告出目标图谱和解卷了组分的图谱的匹配因子。
什么是解卷积(Deconvolution)?NIST AMDIS的定义:“这里所用的术语在广义上是指从一个复杂的混合物中提取信号。 解卷积的过程包括处理噪音、校正漂移、从紧密相邻的共洗脱峰中提取出单个峰等。” (简单讲就是去复杂化)
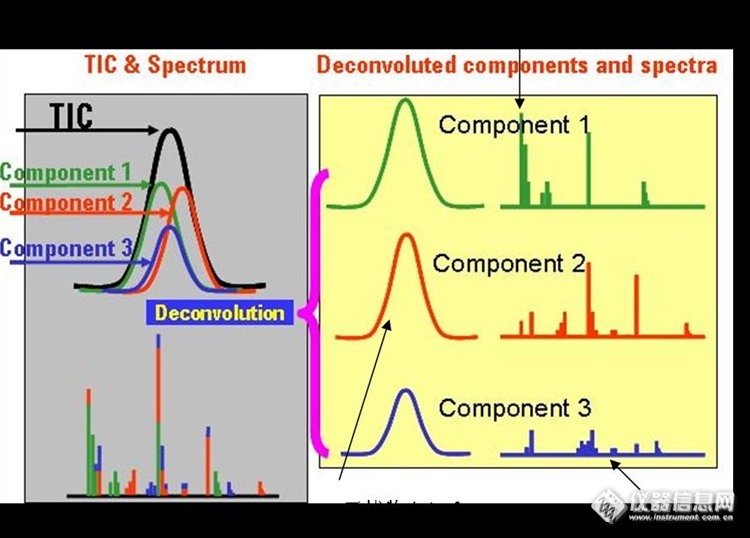
用下面的简图可以解释解卷积过程:
在GC/MS 中,Deconvolution是一种数学技术,它可以将重叠的质谱图“分开”成为“清晰”的单个组分的谱图。图1 是这个过程的简单示意图。这里分别是总离子流色谱图(TIC)和质谱图。与常见的情况一样,这个色谱峰包含了多个重叠在一起的组分,而最高点质谱图实际上也是这些组分的组合图。质谱谱库检索只可能给出一个较差的匹配,而且不能识别所有构成这种组合谱图的单个化合物组分。
![]()
图1 解卷积过程的简单示意图
***************************************************************************
(回顾:在GCMS分离分析时,虽然现代的毛细管色谱柱的分离效率已经非常高,但是还没有一种色谱柱能够能分离开所有化合物,特别是对于香精这类复杂的混合物。虽然可以考虑配有不同极性的柱子来解决不同样品分离问题,但需更换柱子或配备多台仪器,既是这样有些成分复杂的样品仍有部分物质无法分离。另外对于溶剂大峰或其它大面积峰后面或里面的少量组分,或由于基质干扰或掩盖的小峰,也属于不能分离的峰。虽然可以使用多维色谱(MGC-MS或GC/GC-MS)来帮助解决复杂分离一些问题,但许多人并无此仪器。所以有时候不免还会遇到未分离组分的鉴定和定量的情况。)
(12)----难分离共流峰处理实例1
例子,看看这张图的42.376min峰,表面上是一个单个峰,点击峰顶。
![]()
工作站检索后:
![]()
发现是香叶醇,但图谱不纯,有少许m/z60,73等多出来,估计有什么酸存在。
![]()
点击峰的不同部位,发现后面的m/z60,73增加。例如43.3min中m/z60,73就小,43.4min就比较大了。
43.3min的质谱图如下:
![]()
可以看到m/z60,73离子很小。
43.4min的质谱图如下:
![]()
可以看到m/z60,73离子增加不少,比较明显了。直接在后面检索,仍然是香叶醇,无法看到别的组分。这是因为质谱图中的离子仍然以香叶醇为主,其它的离子虽然大了一些,但仍然是一小部分,工作站就无法检索出来了。因为一个在另一个中完全包裹起来,也是不太好选择背景扣除来检索。
看看下面提取
离子色谱图,选择m/z69, 41,60,93, 73, 123离子。
![]()
可以看到m/z60和73在峰的后面部分一点完全包裹在里面了,前面部分稍微少一些。这种情况是比较难以检索的。有时候幸运的话,选择某些地方进行扣除质谱图还可能看到另一个成分,但往往可能比较难。
利用安捷伦工作站的峰纯度分析看看:
![]()
把上面第一个窗口(2#)的提取离子图放大:
![]()
可以看到,和前面提取离子图差不多。
工作站纯度分析结果:
Peak 37
Ret time 42.38
Components 4
Scan ion ion
1 9039.5 69 68
2 9040.2 41
3 9041.0 123
4 9043.8 60
说可能有4个组分,实际分析观察,可能会有两个组分,因为只有m/z60稍微和别的离子所占的位置有所不同,其它离子基本都是一致的。
运行Amdis:
![]()
但也只是看到Geraniol,没有看到别的组分。是什么原因没有出来呢?检查设定参数:
![]()
Resolution: Medium; Sensitivity:Very low; Shape requirements: Medium。
看到灵敏度设置为Very low很低,原来是上个样品组分太复杂,为了减少解卷积运行时间和解析时间而把灵敏度调到最低了。增加灵敏度中low或Medium,才解卷积出来和检索到capronic acid.
![]()
可以看到匹配度还不错,其中反向匹配度为94。核对保留指数也符合,可以确认。
不过在灵敏度越高情况下,amdis的运行时间要比低的情况下的多。可以仅考虑解卷积需要处理的部分峰或区域来进行解卷积。用鼠标左键在所选位置拖曳。然后点击run,这样就仅仅处理放大的所需要的部分进行解卷积和检索。在这种情况amdis的运行速度极快,结果也很简洁。得到了仅仅关心部分的结果。如下图:
![]()
如果想回到原来上一次的取峰范围,在总离子窗口任意位置鼠标右键点击,选择unzoom就行。如果想要回到完整原始的总离子图,则选择UnzoomAll。
![]()